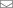[Перевод] Кластеризация с пакетом ClusterR, часть 2
Кластерный анализ или кластеризация — задача группирования набора объектов таким образом, чтобы объекты внутри одной группы (называемой кластером) были более похожи (в том или ином смысле) друг на друга, чем на объекты в других группах (кластерах). Это одна из главных задач исследовательского анализа данных и стандартная техника статистического анализа, применяемая в разных сферах, в т.ч. машинном обучении, распознавании образов, анализе изображений, поиске информации, биоинформатике, сжатии данных, компьютерной графике.
Наиболее известные примеры алгоритмов кластеризации — кластеризация на основе связности (иерархическая кластеризация), кластеризация на основе центров (метод k-средних, метод k-медоидов), кластеризация на основе распределений (GMM — Gaussian mixture models — Гауссова смесь распределений) и кластеризация на основе плотности (DBSCAN — Density-based spatial clustering of applications with noise — пространственная кластеризация приложений с шумом на основе плотности, OPTICS — Ordering points to identify the clustering structure — упорядочивание точек для определения структуры кластеризации, и др.).
В первой части: гауссова смесь распределений (GMM), метод k-средних, метод k-средних в мини-группах.
Метод k-медоидов
Алгоритм k-медоидов (Л. Кауфман, П. Руссо, 1987) — алгоритм кластеризации, имеющий общее с алгоритмом k-средних и алгоритмом смещения медоидов. Алогритмы k-средних и k-медоидов — разделяющие, и оба пытаются минимизировать расстояние между точками предположительно из одного кластера и точкой, назначенной центром этого кластера. В отличие от алгоритма k-средних, метод k-медоидов выбирает точки из набора данных в качестве центров (медоиды или эталоны) и работает с произвольной метрикой расстояний между точками. Полезный инструмент для определения k — ширина контура. Метод k-медоидов более устойчив к шуму и аномальным значениям, чем k-средних, поскольку он минимизирует сумму попарных отклонений, а не сумму квадратов эвклидовых расстояний. Медоид можно определить как объект кластера, чье среднее отклонение от всех остальных объектов в кластере минимально, т.е. это наиболее близкая к центру кластера точка.
Наиболее распространенная реализация кластеризации k-медоидов — алгоритм разделения вокруг медоидов (РАМ — Partitioning Around Medoids). РАМ имеет две фазы: «построить» (BUILD) и «переставить» (SWAP). На фазе BUILD алгоритм ищет хороший набор исходных медоидов, а на фазе SWAP осуществляются все возможные перемещения между BUILD-медоидами и значениями, до тех пор, пока целевая функция не перестанет убывать (Кластеризация в объектно-ориентированном окружении, А. Штруйф, М. Хуберт, П. Руссо, 1997).
В пакете ClusterR функции Cluster_Medoids и Clara_Medoids соответствуют алгоритмам PAM (partitioning around medoids) и CLARA (clustering large applications — кластеризация больших приложений).
В следующем примере кода использую данные mushroom для иллюстрации, как работает метод k-медоидов с метрикой расстояния, отличной от эвклидовой. Данные mushroom состоят из 23 категорийных атрибутов (включая класс) и 8124 значений. В документации к пакету больше информации об этих данных.
Cluster_MedoidsВ качестве входных данных функция Cluster_Medoids может также принимать матрицу отклонений (в дополнение к матрице с данными). В случае данных mushroom, где все переменные категориальные (с двумя или более уникальными значениями), имеет смысл использовать расстояние gower. Расстояние gower применяет разные функции для разных показателей в зависимости от типа (числовой, упорядоченный и неупорядоченный список). Эта метрика отклонения реализована в ряде пакетов R, среди прочих в пакете cluster (функция daisy) и пакете FD (функция gowdis). Я воспользуюсь функцией gowdis из пакета FD, поскольку она также позволяет задать определенные пользователем веса в качестве отдельного фактора.
data(mushroom)
X = mushroom[, -1]
y = as.numeric(mushroom[, 1]) # конвертировать метки в числа
gwd = FD::gowdis(X) # посчитать расстояние 'gower' для факторных переменных
gwd_mat = as.matrix(gwd) # конвертировать расстояния в матрицу
cm = Cluster_Medoids(gwd_mat, clusters = 2, swap_phase = TRUE, verbose = F)
| adjusted_rand_index | avg_silhouette_width |
|---|---|
| 0.5733587 | 0.2545221 |
| predictors | weights |
|---|---|
| cap_shape | 4.626 |
| cap_surface | 38.323 |
| cap_color | 55.899 |
| bruises | 34.028 |
| odor | 169.608 |
| gill_attachment | 6.643 |
| gill_spacing | 42.08 |
| gill_size | 57.366 |
| gill_color | 37.938 |
| stalk_shape | 33.081 |
| stalk_root | 65.105 |
| stalk_surface_above_ring | 18.718 |
| stalk_surface_below_ring | 76.165 |
| stalk_color_above_ring | 27.596 |
| stalk_color_below_ring | 26.238 |
| veil_type | 0.0 |
| veil_color | 1.507 |
| ring_number | 37.314 |
| ring_type | 32.685 |
| spore_print_color | 127.87 |
| population | 64.019 |
| habitat | 44.519 |
weights = c(4.626, 38.323, 55.899, 34.028, 169.608, 6.643, 42.08, 57.366, 37.938,
33.081, 65.105, 18.718, 76.165, 27.596, 26.238, 0.0, 1.507, 37.314,
32.685, 127.87, 64.019, 44.519)
gwd_w = FD::gowdis(X, w = weights) # расстояние 'gower' с применением весов
d_mat_w = as.matrix(gwd_w) # преобразование расстояний в матрицу
cm_w = Cluster_Medoids(gwd_mat_w, clusters = 2, swap_phase = TRUE, verbose = F)
| adjusted_rand_index | avg_silhouette_width |
|---|---|
| 0.6197672 | 0.3000048 |
Clara_Medoids
CLARA (CLustering LARge Applications — кластеризация больших приложений) — очевидный выбор для кластеризации больших наборов данных. Вместо поиска медоидов для всего набора данных — расчет матрицы неподобия — также невыполнимая задача — CLARA берет небольшую выборку и применяет к ней алгоритм РАМ (Partitioning Around Medoids — разделение вокруг медоидов), чтобы сгенерировать оптимальный набор медоидов для этой выборки. Качество полученных медоидов определяется средним неподобием между каждым объектом в наборе данных и медоидом его кластера.
Функция Clara_Medoids в пакете ClusterR использует аналогичную логику, применяя функцию Cluster_Medoids к каждой выборке. Clara_Medoids принимает еще два параметра: samples и sample_size. Первый определяет количество выборок, которые нужно сформировать из исходного набора данных, второй — долю данных в каждой итерации формирования выборок (дробное число между 0.0 и 1.0). Стоит упомянуть, что функция Clara_Medoids не принимает на вход матрицу неподобия, в отличие от функции Cluster_Medoids.
Я применю функцию Clara_Medoids к ранее использованному набору данных mushroom, взяв расстояние Хемминга как метрику неподобия, и сравню время вычисления и результат с результатом функции Cluster_Medoids. Расстояние Хемминга подходит для данных mushroom, т.к. оно применимо к дискретным переменным и определяется, как количество атрибутов, принимающих разные значения для двух сравниваемых экземпляров («Алгоритмы интеллектуального анализа данных: объяснение с R», Пауэл Чикош, 2015, стр. 318).
cl_X = X # скопировать исходные данные
# функция Clara_Medoids принимает только числовые атрибуты
# поэтому сначала привести к числовым
for (i in 1:ncol(cl_X)) { cl_X[, i] = as.numeric(cl_X[, i]) }
start = Sys.time()
cl_f = Clara_Medoids(cl_X, clusters = 2, distance_metric = 'hamming', samples = 5,
sample_size = 0.2, swap_phase = TRUE, verbose = F, threads = 1)
end = Sys.time()
t = end - start
cat('time to complete :', t, attributes(t)$units, '\n')
# время вычисления : 3.104652 сек
| adjusted_rand_index | avg_silhouette_width |
|---|---|
| 0.5944456 | 0.2678507 |
start = Sys.time()
cl_e = Cluster_Medoids(cl_X, clusters = 2, distance_metric = 'hamming', swap_phase = TRUE,
verbose = F, threads = 1)
end = Sys.time()
t = end - start
cat('time to complete :', t, attributes(t)$units, '\n')
# время вычисления : 14.93423 сек
| adjusted_rand_index | avg_silhouette_width |
|---|---|
| 0.5733587 | 0.2545221 |
С использованием расстояния Хемминга и Clara_Medoids, и Cluster_Medoids возвращают примерно одинаковый результат (по сравнению с результатами для расстояния gower), но при этом функция Clara_Medoids работает более чем в четыре раза быстрее, чем Cluster_Medoids, для этого набора данных.
С результатами последних двух фрагментов кода можно построить на графике ширину контура с помощью функции Silhouette_Dissimilarity_Plot. Здесь стоит упомянуть, что неподобие и ширина контура в функции Clara_Medoids — на лучшей выборке, а не на всем наборе данных, как для функции Cluster_Medoids.
# Контурный график для объекта "Clara_Medoids"
Silhouette_Dissimilarity_Plot(cl_f, silhouette = TRUE)
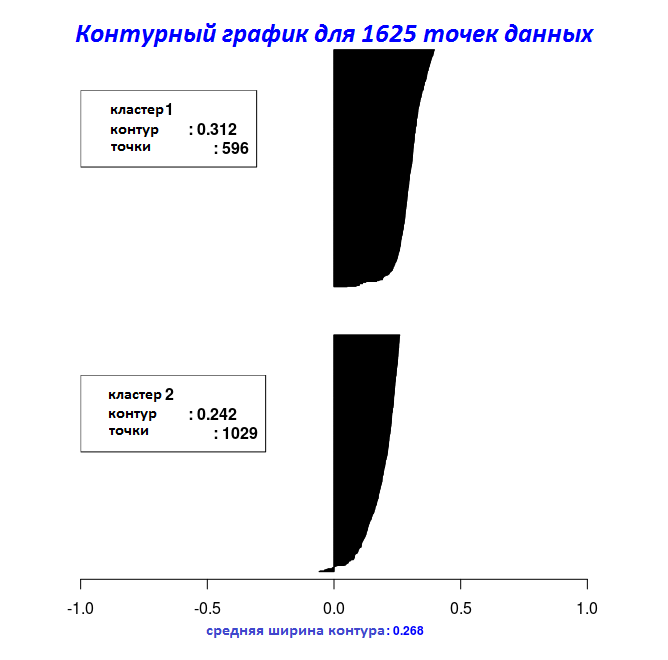
# Контурный график для объекта "Cluster_Medoids"
Silhouette_Dissimilarity_Plot(cl_e, silhouette = TRUE)
Ссылки для функций k-медоидов
Реализация функций k-медоидов (Cluster_Medoids и Clara_Medoids) заняла у меня довольно много времени, поскольку вначале я думал, что начальные медоиды инициализируются так же, как и центры в алгоритме k-средних. Т.к. у меня не было доступа к книге Кауфмана и Руссо, очень помог пакет cluster с подробнейшей документацией. Он включает оба алгоритма, и РАМ (Partitioning Around Medoids — разделение вокруг медоидов), и CLARA (CLustering LARge Applications — кластеризация больших приложений), при желании можно сравнить результаты.
В следующем фрагменте кода сравню функцию pam пакета cluster и Cluster_Medoids пакета ClusterR и полученные медоиды, основываясь на предыдущем примере квантизации.
#====================================
# функция pam пакета cluster
#====================================
start_pm = Sys.time()
set.seed(1)
pm_vq = cluster::pam(im2, k = 5, metric = 'euclidean', do.swap = TRUE)
end_pm = Sys.time()
t_pm = end_pm - start_pm
cat('time to complete :', t_pm, attributes(t_pm)$units, '\n')
# время вычисления : 12.05006 сек
pm_vq$medoids
# [,1] [,2] [,3]
# [1,] 1.0000000 1.0000000 1.0000000
# [2,] 0.6325856 0.6210824 0.5758536
# [3,] 0.4480000 0.4467451 0.4191373
# [4,] 0.2884769 0.2884769 0.2806337
# [5,] 0.1058824 0.1058824 0.1058824
#====================================
# функция Cluster_Medoids пакета ClusterR с использованием 6 потоков (параллелизация доступна с OpenMP)
#====================================
start_vq = Sys.time()
set.seed(1)
cl_vq = Cluster_Medoids(im2, clusters = 5, distance_metric = 'euclidean',
swap_phase = TRUE, verbose = F, threads = 6)
end_vq = Sys.time()
t_vq = end_vq - start_vq
cat('time to complete :', t_vq, attributes(t_vq)$units, '\n')
# время вычисления : 3.333658 сек
cl_vq$medoids
# [,1] [,2] [,3]
# [1,] 0.2884769 0.2884769 0.2806337
# [2,] 0.6325856 0.6210824 0.5758536
# [3,] 0.4480000 0.4467451 0.4191373
# [4,] 0.1058824 0.1058824 0.1058824
# [5,] 1.0000000 1.0000000 1.0000000
#====================================
# функция Cluster_Medoids пакета ClusterR в один поток
#====================================
start_vq_single = Sys.time()
set.seed(1)
cl_vq_single = Cluster_Medoids(im2, clusters = 5, distance_metric = 'euclidean',
swap_phase = TRUE, verbose = F, threads = 1)
end_vq_single = Sys.time()
t_vq_single = end_vq_single - start_vq_single
cat('time to complete :', t_vq_single, attributes(t_vq_single)$units, '\n')
# время вычисления : 8.693385 сек
cl_vq_single$medoids
# [,1] [,2] [,3]
# [1,] 0.2863456 0.2854044 0.2775613
# [2,] 1.0000000 1.0000000 1.0000000
# [3,] 0.6325856 0.6210824 0.5758536
# [4,] 0.4480000 0.4467451 0.4191373
# [5,] 0.1057339 0.1057339 0.1057339
Для этого набора данных (5625 строк и 3 колонки) функция Cluster_Medoids возвращает те же медоиды почти в четыре раза быстрее, чем функция pam, если доступен OpenMP (6 потоков).
Актуальная версия пакета ClusterR доступна в моем Github репозитории, а для баг-репортов, пожалуйста, используйте эту ссылку.